本网讯(生命科学与医学工程学院 叶彬)近日,生命科学与医学工程学院夏俊峰教授、资源与环境工程学院万霞教授开展联合研究,在基于深度学习的物种识别方法研究方面取得重要进展,构建了一种融合多类型DNA条形码与层级注意力网络的物种识别模型,显著提升了从亚纲到种的多层级分类准确性。相关成果以“Multi‐barcoding‐based species identification using a hierarchical attention network with staged curriculum learning”为题,发表于生态学领域顶级期刊Methods in Ecology and Evolution(MEE)(DOI:10.1111/2041-210x.70264)。生命科学与医学工程学院博士后叶彬为论文第一作者,夏俊峰教授、万霞教授为共同通讯作者,南京大学吴岷副教授、日本东北大学千葉聡教授参与了相关研究,安徽大学为论文第一及通讯作者单位。该论文是安徽大学作为第一完成单位在MEE发表的首篇研究论文,标志着学校在“生态学+人工智能”研究领域取得重要进展。
DNA条形码技术已成为生物多样性监测与物种鉴定的重要工具,然而现有深度学习方法多依赖单一COI条形码,难以全面捕捉物种特征,且在高层级分类任务中表现不佳。本研究针对腹足纲中物种最丰富的新进腹足亚纲与异鳃亚纲类群,整合COI、16S、H3、18S、ITS1与ITS2六类DNA条形码,构建了多类型条形码数据集。研究创新性地引入RNA二级结构嵌入表示,并对COI序列补充DNA条形码嵌入特征,以增强特征表征能力。为应对多类型条形码样本覆盖不均衡的挑战,课题组设计了一种三阶段学习策略:首先基于COI数据训练模型,随后冻结部分网络并融合覆盖度较低的条形码数据,最终进行全局微调,得到稳定且高性能的识别模型SnailBaLLsp。该模型采用层级注意力机制,将高层级分类结果作为特征向下传递,从而系统提升从亚纲、目、科、属到物种各层级的鉴定准确率。模型展现出良好的泛化与跨类群迁移能力,在双壳纲数据微调后仍保持较高性能。
该研究首次在物种鉴定深度模型中系统整合多类型条形码与分类层级信息,通过RNA二级结构嵌入与分阶段学习,有效解决了多源条形码数据覆盖不均与层级信息利用不足的难题,为整合分类学与生物多样性监测提供了新的基于深度学习的分子条形码分析框架,推动了物种鉴定方法学的发展。
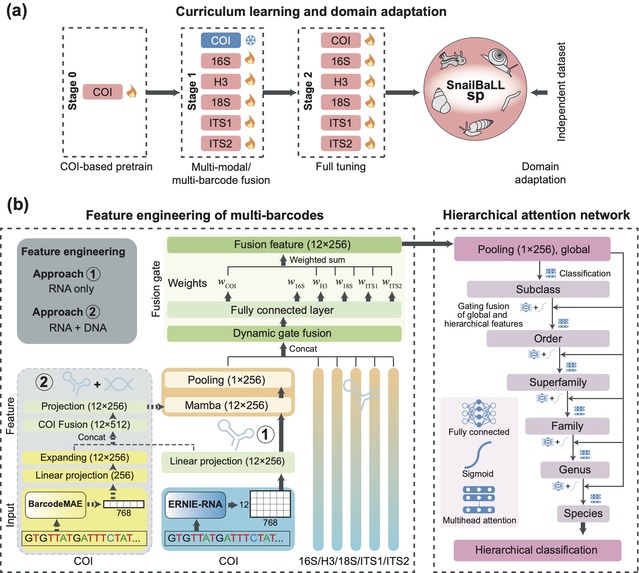
图 多类型DNA条形码层级物种分类模型SnailBaLLsp的模型架构




